Note
Go to the end to download the full example code. or to run this example in your browser via Binder
分位数回归#
此示例说明了分位数回归如何预测非平凡的条件分位数。
左图显示了误差分布为正态分布但具有非恒定方差(即异方差性)的情况。
右图显示了一个不对称误差分布的示例,即帕累托分布。
# 作者:scikit-learn 开发者
# SPDX-License-Identifier: BSD-3-Clause
数据集生成#
为了说明分位数回归的行为,我们将生成两个合成数据集。这两个数据集的真实生成随机过程将由相同的期望值组成,并与单个特征 x 存在线性关系。
import numpy as np
rng = np.random.RandomState(42)
x = np.linspace(start=0, stop=10, num=100)
X = x[:, np.newaxis]
y_true_mean = 10 + 0.5 * x
我们将通过改变目标 y 的分布来创建两个后续问题,同时保持相同的期望值:
在第一种情况下,添加了异方差正态噪声;
在第二种情况下,添加了非对称帕累托噪声。
y_normal = y_true_mean + rng.normal(loc=0, scale=0.5 + 0.5 * x, size=x.shape[0])
a = 5
y_pareto = y_true_mean + 10 * (rng.pareto(a, size=x.shape[0]) - 1 / (a - 1))
让我们首先可视化数据集以及残差 y - mean(y) 的分布。
import matplotlib.pyplot as plt
_, axs = plt.subplots(nrows=2, ncols=2, figsize=(15, 11), sharex="row", sharey="row")
axs[0, 0].plot(x, y_true_mean, label="True mean")
axs[0, 0].scatter(x, y_normal, color="black", alpha=0.5, label="Observations")
axs[1, 0].hist(y_true_mean - y_normal, edgecolor="black")
axs[0, 1].plot(x, y_true_mean, label="True mean")
axs[0, 1].scatter(x, y_pareto, color="black", alpha=0.5, label="Observations")
axs[1, 1].hist(y_true_mean - y_pareto, edgecolor="black")
axs[0, 0].set_title("Dataset with heteroscedastic Normal distributed targets")
axs[0, 1].set_title("Dataset with asymmetric Pareto distributed target")
axs[1, 0].set_title(
"Residuals distribution for heteroscedastic Normal distributed targets"
)
axs[1, 1].set_title("Residuals distribution for asymmetric Pareto distributed target")
axs[0, 0].legend()
axs[0, 1].legend()
axs[0, 0].set_ylabel("y")
axs[1, 0].set_ylabel("Counts")
axs[0, 1].set_xlabel("x")
axs[0, 0].set_xlabel("x")
axs[1, 0].set_xlabel("Residuals")
_ = axs[1, 1].set_xlabel("Residuals")
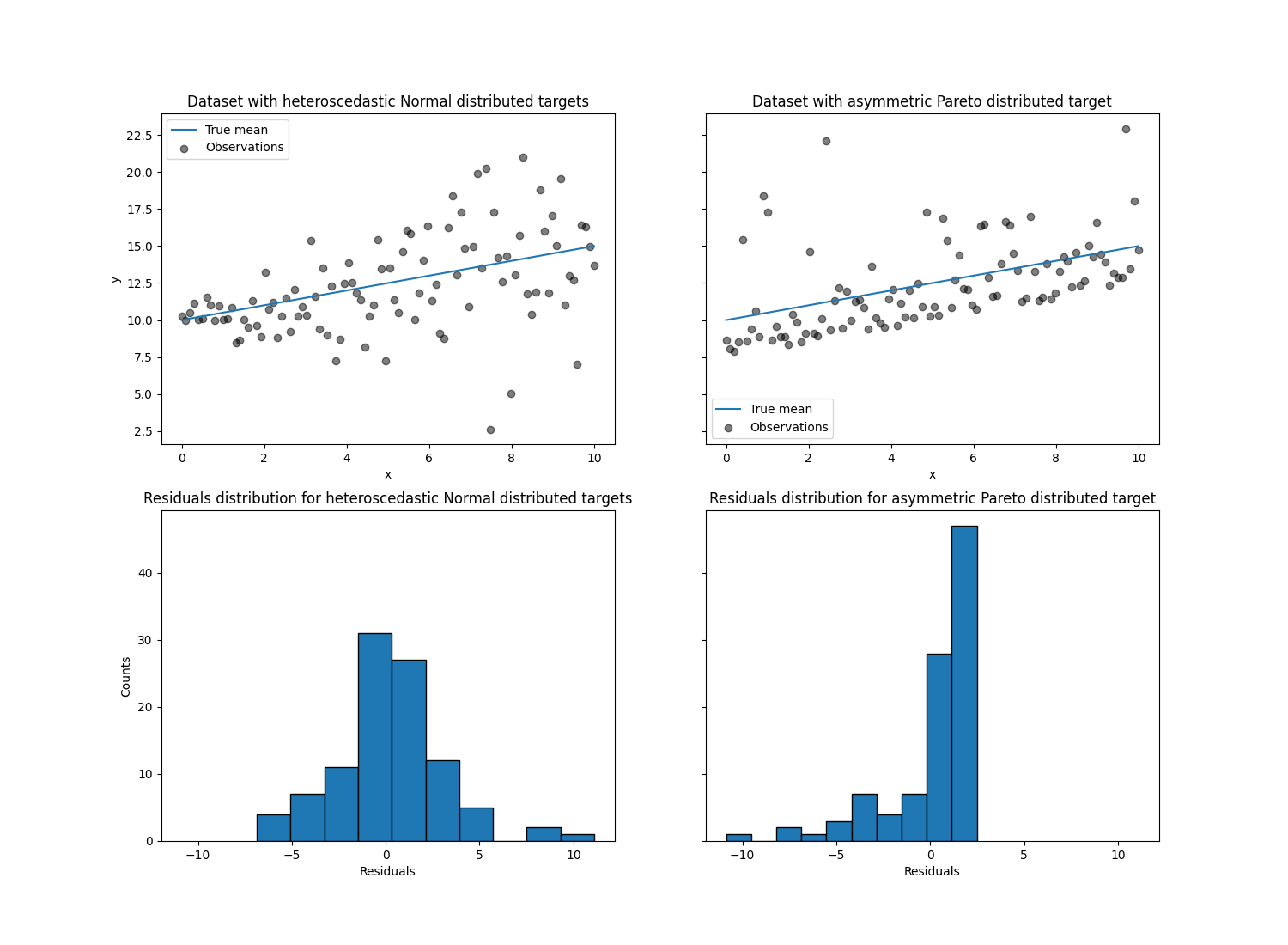
对于异方差正态分布的目标,我们观察到当特征 x 的值增加时,噪声的方差也在增加。
对于不对称的帕累托分布目标,我们观察到正残差是有界的。
这些类型的噪声目标使得通过:class:~sklearn.linear_model.LinearRegression 进行估计的效率降低,即我们需要更多的数据才能获得稳定的结果,此外,大的异常值会对拟合系数产生巨大影响。(换句话说:在方差恒定的情况下,普通最小二乘估计量随着样本量的增加会更快地收敛到*真实*系数。)
在这种不对称的情况下,中位数或不同的分位数可以提供额外的见解。此外,中位数估计对异常值和重尾分布更加稳健。但请注意,极端分位数是由非常少的数据点估计的。95%分位数大致由5%最大值估计,因此对异常值也有些敏感。
在本教程的剩余部分中,我们将展示如何在实践中使用 QuantileRegressor ,并提供对拟合模型属性的直观理解。最后,我们将比较 QuantileRegressor 和 LinearRegression 。
拟合 QuantileRegressor
在本节中,我们希望估计条件中位数以及固定在5%和95%的低分位数和高分位数。因此,我们将得到三个线性模型,每个分位数对应一个模型。
我们将使用5%和95%的分位数来查找训练样本中超出中心90%区间的异常值。
from sklearn.utils.fixes import parse_version, sp_version
# 这是为了避免旧版本的SciPy不兼容。如果使用较新版本的SciPy,你应该使用 `solver="highs"` 。
solver = "highs" if sp_version >= parse_version("1.6.0") else "interior-point"
from sklearn.linear_model import QuantileRegressor
quantiles = [0.05, 0.5, 0.95]
predictions = {}
out_bounds_predictions = np.zeros_like(y_true_mean, dtype=np.bool_)
for quantile in quantiles:
qr = QuantileRegressor(quantile=quantile, alpha=0, solver=solver)
y_pred = qr.fit(X, y_normal).predict(X)
predictions[quantile] = y_pred
if quantile == min(quantiles):
out_bounds_predictions = np.logical_or(
out_bounds_predictions, y_pred >= y_normal
)
elif quantile == max(quantiles):
out_bounds_predictions = np.logical_or(
out_bounds_predictions, y_pred <= y_normal
)
现在,我们可以绘制三个线性模型,并区分出在中心90%区间内的样本和在该区间外的样本。
plt.plot(X, y_true_mean, color="black", linestyle="dashed", label="True mean")
for quantile, y_pred in predictions.items():
plt.plot(X, y_pred, label=f"Quantile: {quantile}")
plt.scatter(
x[out_bounds_predictions],
y_normal[out_bounds_predictions],
color="black",
marker="+",
alpha=0.5,
label="Outside interval",
)
plt.scatter(
x[~out_bounds_predictions],
y_normal[~out_bounds_predictions],
color="black",
alpha=0.5,
label="Inside interval",
)
plt.legend()
plt.xlabel("x")
plt.ylabel("y")
_ = plt.title("Quantiles of heteroscedastic Normal distributed target")
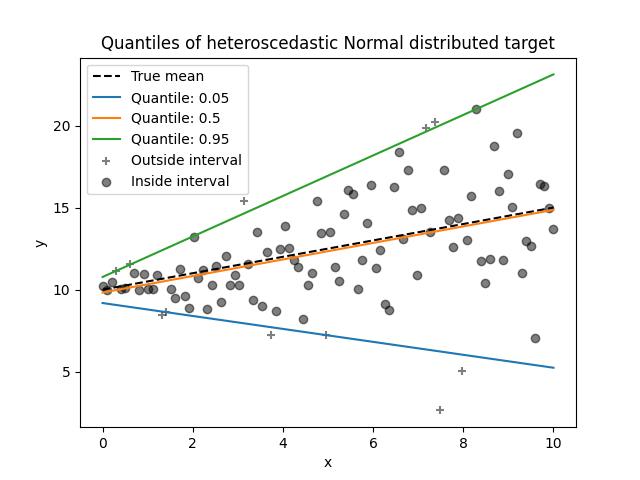
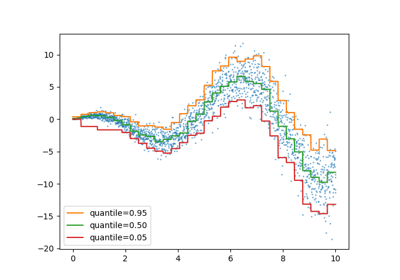
由于噪声仍然是正态分布的,特别是对称的,真实条件均值和真实条件中位数是一致的。实际上,我们看到估计的中位数几乎与真实均值相符。我们观察到噪声方差增加对5%和95%分位数的影响:这些分位数的斜率非常不同,并且随着 x 的增加,它们之间的区间变得更宽。
为了更直观地理解5%和95%分位数估计量的含义,可以计算在预测分位数(在上图中用叉号表示)之上和之下的样本数量,假设我们总共有100个样本。
我们可以使用非对称帕累托分布目标重复相同的实验。
quantiles = [0.05, 0.5, 0.95]
predictions = {}
out_bounds_predictions = np.zeros_like(y_true_mean, dtype=np.bool_)
for quantile in quantiles:
qr = QuantileRegressor(quantile=quantile, alpha=0, solver=solver)
y_pred = qr.fit(X, y_pareto).predict(X)
predictions[quantile] = y_pred
if quantile == min(quantiles):
out_bounds_predictions = np.logical_or(
out_bounds_predictions, y_pred >= y_pareto
)
elif quantile == max(quantiles):
out_bounds_predictions = np.logical_or(
out_bounds_predictions, y_pred <= y_pareto
)
plt.plot(X, y_true_mean, color="black", linestyle="dashed", label="True mean")
for quantile, y_pred in predictions.items():
plt.plot(X, y_pred, label=f"Quantile: {quantile}")
plt.scatter(
x[out_bounds_predictions],
y_pareto[out_bounds_predictions],
color="black",
marker="+",
alpha=0.5,
label="Outside interval",
)
plt.scatter(
x[~out_bounds_predictions],
y_pareto[~out_bounds_predictions],
color="black",
alpha=0.5,
label="Inside interval",
)
plt.legend()
plt.xlabel("x")
plt.ylabel("y")
_ = plt.title("Quantiles of asymmetric Pareto distributed target")
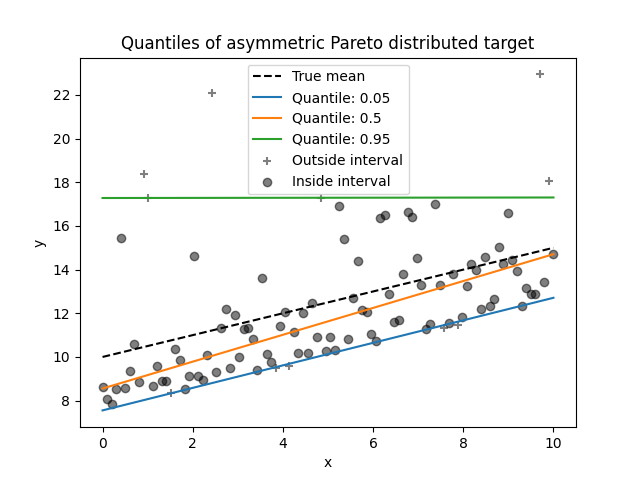
由于噪声分布的不对称性,我们观察到真实均值和估计的条件中位数是不同的。我们还观察到每个分位数模型都有不同的参数,以更好地拟合所需的分位数。请注意,理想情况下,所有分位数在这种情况下应该是平行的,这在数据点更多或分位数不那么极端时(例如10%和90%)会更加明显。
比较 QuantileRegressor 和 LinearRegression
在本节中,我们将详细讨论 QuantileRegressor 和 LinearRegression 所最小化的误差之间的差异。
实际上,LinearRegression 是一种最小二乘法,旨在最小化训练目标和预测目标之间的均方误差(MSE)。相比之下, quantile=0.5 的 QuantileRegressor 则是最小化平均绝对误差(MAE)。
让我们首先计算这些模型的训练误差,包括均方误差和平均绝对误差。我们将使用不对称的帕累托分布目标来使其更有趣,因为均值和中位数不相等。
from sklearn.linear_model import LinearRegression
from sklearn.metrics import mean_absolute_error, mean_squared_error
linear_regression = LinearRegression()
quantile_regression = QuantileRegressor(quantile=0.5, alpha=0, solver=solver)
y_pred_lr = linear_regression.fit(X, y_pareto).predict(X)
y_pred_qr = quantile_regression.fit(X, y_pareto).predict(X)
print(
f"""Training error (in-sample performance)
{linear_regression.__class__.__name__}:
MAE = {mean_absolute_error(y_pareto, y_pred_lr):.3f}
MSE = {mean_squared_error(y_pareto, y_pred_lr):.3f}
{quantile_regression.__class__.__name__}:
MAE = {mean_absolute_error(y_pareto, y_pred_qr):.3f}
MSE = {mean_squared_error(y_pareto, y_pred_qr):.3f}
"""
)
Training error (in-sample performance)
LinearRegression:
MAE = 1.805
MSE = 6.486
QuantileRegressor:
MAE = 1.670
MSE = 7.025
在训练集上,我们看到 QuantileRegressor 的 MAE 低于 LinearRegression 。与此相反,LinearRegression 的 MSE 低于 QuantileRegressor 。这些结果证实了 MAE 是 QuantileRegressor 最小化的损失,而 MSE 是 LinearRegression 最小化的损失。
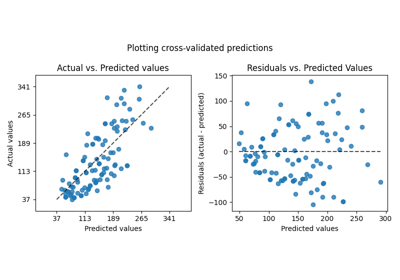
我们可以通过查看通过交叉验证获得的测试误差来进行类似的评估。
from sklearn.model_selection import cross_validate
cv_results_lr = cross_validate(
linear_regression,
X,
y_pareto,
cv=3,
scoring=["neg_mean_absolute_error", "neg_mean_squared_error"],
)
cv_results_qr = cross_validate(
quantile_regression,
X,
y_pareto,
cv=3,
scoring=["neg_mean_absolute_error", "neg_mean_squared_error"],
)
print(
f"""Test error (cross-validated performance)
{linear_regression.__class__.__name__}:
MAE = {-cv_results_lr["test_neg_mean_absolute_error"].mean():.3f}
MSE = {-cv_results_lr["test_neg_mean_squared_error"].mean():.3f}
{quantile_regression.__class__.__name__}:
MAE = {-cv_results_qr["test_neg_mean_absolute_error"].mean():.3f}
MSE = {-cv_results_qr["test_neg_mean_squared_error"].mean():.3f}
"""
)
Test error (cross-validated performance)
LinearRegression:
MAE = 1.732
MSE = 6.690
QuantileRegressor:
MAE = 1.679
MSE = 7.129
我们在样本外评估中得出了类似的结论。
Total running time of the script: (0 minutes 0.289 seconds)
Related examples